作者:李覺白/有勁生物科技
疾病表現型 (disease phenotype)所對應的基因型 (genotype),對科學家了解疾病致病機制及生物體代謝路徑來說是很重要的資訊。隨著基因體技術的進步,不同解析度下被找到的變異基因型與疾病表現型的關聯快速大量被發現,並登記在生醫資料庫中供使用者查詢。本篇簡介近二十多年來應用在基因型辨識的技術及目前常使用到的基因型對應疾病表現型資料庫。
作者:李覺白/有勁生物科技
疾病表現型 (disease phenotype)所對應的基因型 (genotype),對科學家了解疾病致病機制及生物體代謝路徑來說是很重要的資訊。隨著基因體技術的進步,不同解析度下被找到的變異基因型與疾病表現型的關聯快速大量被發現,並登記在生醫資料庫中供使用者查詢。本篇簡介近二十多年來應用在基因型辨識的技術及目前常使用到的基因型對應疾病表現型資料庫。
作者:沈淑華/有勁生物科技
癌症發生的真正原因一直未有明確答案,因此癌症研究向來是生醫學界的熱門話題。近幾年科學界大量投入「基因體」研究,進而發現「基因突變或缺陷」有可能是癌症發生的關鍵。基因是主宰體內細胞生長的基礎,一旦基因發生問題,導致細胞異常增生累積,就有可能形成腫瘤。
作者:洪郁豪/有勁生物科技
DNA 的甲基化現象研究一直以來是個熱門的話題,脊椎動物最常發生在CpG中Cytosine的五號碳上,植物或是哺乳類動物幹細胞上則常見發生在 CHG及CHH上。當甲基化的位置在promoter上時,通常會 down-regulate 下游基因表現,這種基因調控的功能,與多種細胞分化、抗腫瘤基因、生長發育等等相關。
近年來使用次世代定序儀技術發展了數種研究DNA 的甲基化現象的方式,分別是使用 Bisulphite conversion 特性進行全基因體定序的 whole-genome bisulphite sequencing (WG-BS)、使用 probe 附加 target enrichment 的bisulphite sequencing (Targeted-BS)、使用抗體針對甲基化區域做免疫沉降的 methyled DNA immunoprecipitation sequencing (MeDIP-seq)及將 Bisulphite conversion 特性與抗體做免疫沉降混合的 methyled DNA immunoprecipitation bisulphfite sequencing (MeDIP-BS) (圖一)。
作者:洪郁豪/有勁生物科技
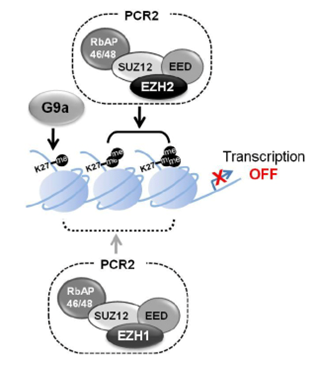
過去的研究顯示,基因表現調控的方式與 DNA甲基化以及 histone modification 有重要的關係,但它們彼此之間是如何透過交互作用而調控基因表現卻不是十分充分的被研究。DNA的甲基化現象是經由 DNA methyltransferase 將甲基經催化反應標誌在 DNA 上,通常能抑制轉錄作用;而histone 經modification 後能改變 chromatin 結構進而影響基因表現,其中由 Polycomb-repressive complex 2 (PRC2) 中的 histone methyltransferase EZH2 催化 H3K27 甲基化形成的 H3K27me3,科學家們發現總是可在一部份被抑制的基因 promoter 上觀察到,因此,H3K27me3可能也與抑制基因表現脫離不了關係,在過去研究中也一直認為 PRC2 與 H3K27me3與抑制基因表現具關聯性 (圖一)。
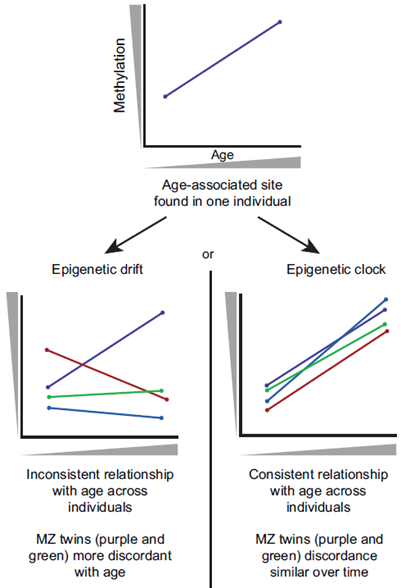
有人透過生物電阻分析儀器估算身體年齡,也有人可以透過膚質檢測計了解肌膚的狀態,目的都是要了解老化的情形,並了解自己是否保養得宜,更重要的是從古迄今,人們害怕變老、害怕死亡及好奇壽命的長短。科學家抽絲剝繭深入的探索並揭露生命的秘密,影響老化的機制,可能包括了DNA本身衰老 (senescence)、端粒縮短 (telomere shortening)、基因表現改變等等。基因外修飾被視為影響基因表現的重要角色,基因外修飾的特點是不會改變DNA本身之序列,而是透過DNA甲基化、histone acetylation等方式,去影響基因的表現。
DNA甲基化在基因體上的總量以及在特定的某些位點的變異程度,會隨著生命週期的發展而有所改變。在新生兒血液中,發現DNA甲基化的量低於各個生命期並在出生後的第一年,DNA甲基化才會開始增加。而增加的位置通常發生在CpG island shores and shelves、enhancers、promoters lacking CpG islands。兒童及青少年的相關研究較少,因此DNA甲基化程度,仍不是很清楚。在成人期則在血液及腦部中,發現DNA甲基化快速增加並且穩定下來,且隨著年紀增加,個體差異會越來越大。成人後期,血中DNA甲基化程度會隨著老化的增加而降低,然而,更深入分析時則發現,原先甲基化較低的區域,如與啟動子(promotor)有關的CpG islands,會隨著老化而增加DNA甲基化,相反的,原先有較高甲基化的區域,如intergenic nonisland CpGs 則是傾向失去甲基。
 2014年的6月初,由美國非營利組織 The ALS Association(美國漸凍人協會)發起的「冰桶挑戰」,於社交網路上讓許多知名人士接力響應,為肌萎縮性脊髓側索硬化症(Amyotrophic lateral sclerosis,簡稱ALS)的研究募集到了資金,也讓人們重新認識這種罕見疾病。這種疾病通常被稱作葛雷克氏症(Lou Gehrig’s disease)。目前,美國大約有3萬人患有ALS,在台灣也約有1千多人患有ALS,罹患ALS患者的脊髓、腦幹或大腦運動皮脂的運動神經元會慢慢退化,造成全身肌肉無力、萎縮,最終會導致患者徹底癱瘓,但患者的思維仍會保持敏捷。確診後,患者的壽命通常只有兩到五年。也有少數的病人能存活超過50年,例如世界知名理論物理學家霍金現年已經73歲,但他於21歲時就被診斷罹患了ALS。
2014年的6月初,由美國非營利組織 The ALS Association(美國漸凍人協會)發起的「冰桶挑戰」,於社交網路上讓許多知名人士接力響應,為肌萎縮性脊髓側索硬化症(Amyotrophic lateral sclerosis,簡稱ALS)的研究募集到了資金,也讓人們重新認識這種罕見疾病。這種疾病通常被稱作葛雷克氏症(Lou Gehrig’s disease)。目前,美國大約有3萬人患有ALS,在台灣也約有1千多人患有ALS,罹患ALS患者的脊髓、腦幹或大腦運動皮脂的運動神經元會慢慢退化,造成全身肌肉無力、萎縮,最終會導致患者徹底癱瘓,但患者的思維仍會保持敏捷。確診後,患者的壽命通常只有兩到五年。也有少數的病人能存活超過50年,例如世界知名理論物理學家霍金現年已經73歲,但他於21歲時就被診斷罹患了ALS。
ALS的患者可分為家族性遺傳及偶發性的患者,其中有約10%的患者為家族遺傳性ALS患者,已知約有13個基因與基因座發生缺陷的相關效應。(可參考中華民國運動神經元疾病病友協會的介紹)。
何謂ChIP-Seq?
ChIP–seq ( Chromatin immunoprecipitation sequencing )是指染色質免疫沉澱後,所獲得的DNA片段進行高通量定序,並將此片段利用生物資訊的軟體對回至基因體,可以瞭解DNA-binding proteins及histone modifications的狀況,進而得知染色質及相结合的調控因子之間的相互作用關係。
ChIP-chip與ChIP-Seq差異?
DNA 的甲基化現象 (DNA methylation) 是表觀基因體機制 (epigenetic mechanism) 中的一種,其對於真核生物基因調控而言是非常重要,真核生物基因的 5’ 端,常可見到高密度的雙鹼基 C-G 存在,其被稱為 CpG islands,而其中大約有 2-7%的胞嘧啶 (Cytosine),藉著 DNA 甲基轉移酶 (DNA methyltransferase) 作用下被甲基化。另外,在原核生物中,DNA 甲基轉移酶主要的功用是用作保護自己 DNA的手段,以避免遭受內生的限制酶剪切,而利用限制酶對付外來侵略性的 DNA,而在真核生物中,也有藉由 DNA 甲基化來避免 retrovirus 表現的防禦機制被報導過,但無論如何,最主要的功能還是在於調控基因表現為主。
研究 DNA methylation 現象的實驗方法有許多種,包括重亞硫酸鹽 (bisulfate) 和非重亞硫酸鹽 (non-bisulfite) 的方法,在樣品處理重亞硫酸鹽的部分,胞嘧啶(Cytosine) 會脫去胺基變成尿嘧啶 (Uracil),但是被甲基化的胞嘧啶不會被改變,經 PCR 放大之後定序,比對原有參考物種序列,可以知道哪些胞嘧啶發生了點突變,沒有突變的胞嘧啶,有可能就是被甲基化的候選,在非使用重亞硫酸鹽的方法中,主要是使用對甲基化敏感的限制酵素來當作工具,隨後搭配AFLP (amplified fragment length polymorphism) 技術來做研究。
2008 年,致力於開發 Optical mapping技術的 Schwartz 團隊,發表一篇利用這項技術來研究DNA 甲基化現象的期刊,他們首先在 E. coli 上做測試,當發現這項結合可行之後,將頭腦動到真核生物中,同樣被熱門研究的人類染色體上。在真核生物上進行 Optical mapping 時,較於原核生物容易出現一個問題
,即是不一定有能製造出足夠切位的限制酶,當電腦分析切位不足的單分子 DNA 影像時,無法轉換成鑑別性高的條帶 (barcode) 資訊,因此會面臨片段重組上的難題。在他們進行人類第九號染色體DNA 甲基化現象研究時,嘗試使用 2 種以上的限制酶來克服上述的問題,一種是在非重亞硫酸鹽研究方法中提到對甲基化敏感的限制酶:EagI (C^GGCCG),另一種是辨識切位完全與前一種不會重疊、對於 CMepG 甲基化不敏感、用來製造條帶資訊的限制酶:SwaI (ATTT^AAAT)。SwaI 在人類基因體序列中,按照電腦分析大致上能切碎成平均約 15 kb 的片段,而 EagI 在不考慮甲基化情形下,按照電腦分析大致上能切碎成平均約 32 kb 的片段。如同預期的,EagI 的辨識切位可涵蓋了 78%、大約 27,437 個 CpG islands,而其中大約一半的是獨一切位,將這項預測結果搭配上用來製造條帶的SwaI 實際進行Optical mapping 實驗,電腦記錄分析了實際實驗後的結果 (圖一),並組成了一些 contig 片段,再與電腦模擬片段去做平行比較。
之前我們探討了兩種會造成組裝過程產生錯誤結果的因素,這次我們要再來探討第三種因素。
3.重複區域Repeat region

假設我們將NGS的定序資料隨機抽取出三條reads (紅色線條),發現這三條reads的尾端(藍色區域)均有相同的序列,所以藍色區域即為repeat region。當遇到這種情況時,程式會無法判定究竟哪兩條reads應該要組合在一起。但是假如我們使用paired-end reads,即可解決此一問題。如圖示:
目前 De Novo 序列組裝演算法有兩種, 一種稱為 overlap-layout-consensus , 簡稱 OLC. 另一種則是 de-bruijn-graph , 簡稱 DBG.
OLC 方法較為直觀, 先是將所有的 reads 做兩兩比對( pair-wise alignment ), 找出 reads 重疊( overlap )的區域, 再以圖學( graph theory )的方式呈現( layout ) reads 之間的重疊的關係, 以節點( vertex )表示 read, 邊( edge )表示 read 之間的重疊, 見圖一.
最後, 我們要將圖轉為序列. 這個問題, 和一個古典的問題相同, 就是漢米爾頓路徑問題 ( Hamiltonian Path Problem ), 如何走過圖上每一個節點, 而且每一個節點只經過一次?
目前組裝以OLC演算法為基礎的軟體有 Arachne, CAP3, Phrap, Newbler 等.
當我們想要研究一個物種,可是卻發現這個物種的序列資料 (DNA or RNA) 並不存在於世界上現有的資料庫。當我們遇到這種情況,便可以利用 NGS 的資料來進行所謂的 de novo assembly,藉此幫助我們獲取此物種的序列內容。而一個常見的 de novo assembly 流程概念如下:
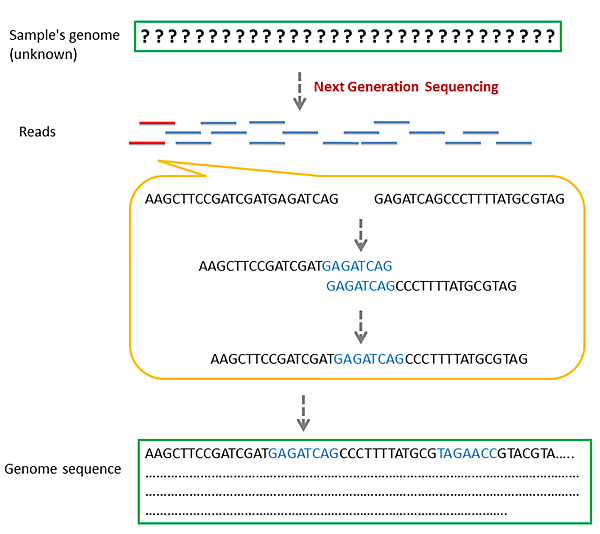
上圖表示將 NGS 的定序資料隨機抽取出兩條 reads (紅色線條),觀察此 reads 的尾端序列是否相同。如有某區域相同(藍色序列),則將此區域的序列合併連結起來,最後獲得一條更長的序列。透過這樣不斷的重複尋找,最終我們便可以將 reads 的資料還原回 genome 序列。
上述的過程是一個理想狀態,然而事實上有許多因素會造成我們組裝困難,我們將這些因素條列如後:
NGS 技術近年來協助科學家解開許多以往醫學上無法破解的謎團,其中包含致病分子機轉、感染性微生物特性及流行病學等,也使得科學家對於醫學的治療及預防提出許多新穎的想法,除此之外,在臨床分子診斷技術上,科學家及醫師皆認為 NGS 技術未來勢必可以成為診斷的利器。然而,NGS技術所提供的資訊,在實際臨床上似乎少有病患直接受惠的案例,直到2011年獲得普立茲獎的一篇文章報導以 Exome sequencing 協助醫師解救一名叫做Nicholas Volker的4歲小孩故事1,並且此案例被發表在 Genetics in Medicine 上2。
Nicholas Volker首先在其肛門附近不明原因地出現許多簍管,使得排泄物不斷湧出,並且出現感染發炎現象,為防止致命性的細菌感染及傷口惡化,醫師對Nicholas Volker做了結腸造口術,期望他的傷口能夠免除自體排泄物的感染,但出乎意料之外的事情發生了,就在結腸造口術的位置出現新的簍管且有嚴重的發炎現象,而這些發炎的區域漸漸地侵襲Nicholas Volker的整個大腸(圖一),使得醫師不得不切除小孩所有的大腸,然而,不久之後小腸也開始出現簍管及發炎的現象,Nicholas Volker的體力越來越糟,若不快速找出病因,尋求有效的治療方法,生命可能不保。

此時傳統的病理切片檢查及免疫學檢查所提供的訊息,僅顯示小孩的病症並非是一般的發炎性腸病 (inflammatory bowel disease),但仍無法知道確切的病因,後來醫師利用 Exome sequencing 技術,分析小孩 exome 中的 nonsynonymous variants,發現小孩的 X-linked inhibitor of apoptosis gene 變異是造成小孩腸子不斷發炎最有可能的原兇。有了NGS提供的這個資訊,醫師很明確地為小孩進行骨髓移植,移植後的小孩目前已恢復健康,並且期待長大成人迎接這個美好的世界。
心肌病變可分為擴張型(dilated)、肥厚型(hypertrophic)或限制型(restrictive)三種,而這些心肌病變的臨床表現是依收縮壓或舒張壓的功能障礙而有所不同,現今
擴張型心肌病變普遍被認為是心臟衰竭與心臟移植的問題所在。目前研究顯示,
使用 NGS 系統應用在物種全基因體上定序上是已發展成熟的技術,然而在真核生物的研究方面,有著高等生物基因體過於龐大複雜的難題存在,在過去,科學家們想研究物種的基因體特定區域時,往往只能小部份的使用 PCR 增幅目標區域並定序之,如今結合上 Exome Capture 技術以及 NGS 系統,能夠讓科學家們專注在研究目標的表現基因上,還能以更便宜的價格,獲得較全基因體定序深度更深的序列資料。
以人類基因體舉例來說,30 億個鹼基對的全基因體序列,Exome 部份僅有其中的 3000 萬,這表示許多科學家們著手研究一項研究主題時,可能僅是對其中 1% 的序列感興趣,因此出現了利用 DNA 雜合原理為基礎的 Exome Capture 技術。下圖為 Exome Capture 的流程圖,我們將製備完成的 DNA library,在鹼的環境下打斷氫鍵變成單股,在加入掛上 Biotin 的單股 DNA Exome probe,使得基因體中的 Exome 部份被這些 probe 雜合上,其後再使用帶有磁珠的 Streptavidin,留下 Exome 洗去不需要的基因部分。除此之外尚有其他三種 Exome Capture 的方式,有的需要 DNA polymerase 參予,不過原理仍大同小異,最重要的部分,仍然是 Exome Probe 的設計,要利用小片段的 DNA (ex: 95 mer) 專一性的抓住較大片段的 DNA (ex: 350 mer),是需要經過精密的設計以及評估的。

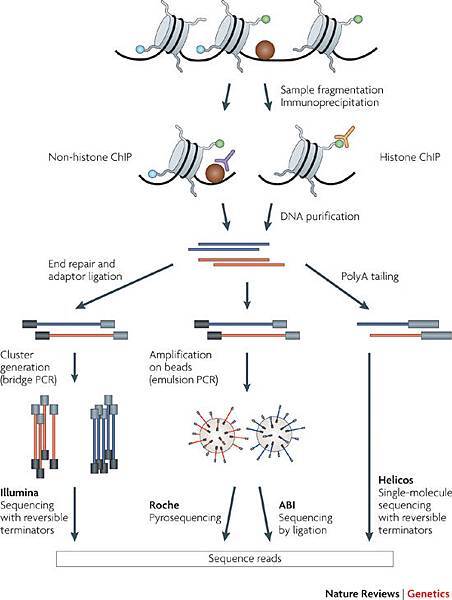
ChIP-sequencing是研究蛋白質與DNA互動的一種方法,是利用抗體與抗原結合的特性,將蛋白質與互動的DNA抓下,再透過DNA純化的方法,取得與蛋白質互動的DNA,然後透過次世代定序的技術來得到該DNA正確的序列。
其實驗流程為: 進行免疫沉澱,加入對目標蛋白質具高專一性與靈敏性的抗體,抓下蛋白質與其所附著的DNA,透過DNA純化去除蛋白質得到DNA,然後進行定序。
致病性微生物的來源管控及監測對於預防群體感染是相當重要的,傳統上須藉由比較微生物基因體結構上的相似度來找尋感染的源頭,常見的分子檢測方式為PFGE。Optical mapping能在短時間內得到微生物的全基因體限制酶切位圖譜, 因此,在比較不同來源微生物的基因體結構上,能得到比PFGE更精確且詳盡的資訊。目前Optical mapping在管控致病性微生物上,對於找尋醫院內部集體感染抗藥性金黃色葡萄球菌(Methicillin Resistant Staphylococcus aureus, MRSA)的傳播來源及細菌抗藥基因和毒性基因的分析,皆能提供即時且精確的資訊。
抗藥性金黃色葡萄球菌是醫院院內感染最常見的菌種,免疫力較差的住院患者常一旦被感染後,容易因為敗血症而導致死亡,因此,抗藥性金黃色葡萄球菌在醫院內的感染管控是相當重要的。下圖為以optical mapping找尋感染來源的實際案例,以不同病房內所採集到的抗藥性金黃色葡萄球菌之限制酶切位圖譜,與被感染的患者身上收集到的細菌之切位圖譜做相似度的比較,能準確的找出病人被感染之來源病房,並且得以針對特定病房做消毒及管控,進而達到防止集體感染之目的。

在進行 de novo sequencing 時,假如我們只利用NGS的資料要將全基因體序列組裝起來,通常要非常高的覆蓋率 (coverage) 才可能將基因體組裝起來,但是,如此高的覆蓋率,不但定序費用相當高,而且面對龐大的資料量,組裝所需的硬體需求將是我們所面臨的第一個難題,組裝所需的漫長運算時間,則是另一個難題,此外,組裝錯誤亦無法被查覺。
利用 Optical mapping 可以更有效率地進行 de novo sequencing ,以更低的成本,更快的速度組完全基因體序列。
首先,我們利用 Optical mapping 建立全基因體的圖譜。
一般在做全基因體比較時,通常會先得到全基體的序列,然後再比較基因體之間的差異。
但是,當我們還不知道這些基因體是否存在差異前,貿然進行全基因體定序,倘若結果未能如我們預期,定序所花費大量的人力、物力與金錢無異是種浪費。
在定序前,我們可以先以 Optical mapping 來分析我們要比較的基因體:
菌株分型(strain typing)是分析菌株差異性常用的方法。
過去常用的方法是 PFGE (Pulsed Field Gel Electrophoresis),但是PFGE的缺點是
使用 optical mapping 的話,即便是相近的菌株,我們仍能有效地加以區分,另外,除了分型之外,我們還能利用全基因體的比較而得知不同菌株間 insertion、deletion與基因轉置等等現象。
下圖即為 optical mapping 分析 strain typing 的結果,圖中兩菌株間的線條所標示之處即為菌株間相異之處。
Optical mapping 是利用限制酶去裁切單分子DNA,產生單分子DNA圖譜,然後將許多單分子DNA圖譜組裝起來,以得到全基因體圖譜的一種技術。
其實驗步驟如下:
一、以PDMS組成的微流道,利用毛細現象的原理,將DNA拉直,由於微流道下方的玻片為帶有正電之玻片,利用DNA帶負電的特性,將DNA固定在特殊玻片上(正負電相吸),此時,我們會得到一條筆直的單分子DNA。
