作者:沈淑華/有勁基因
腦膜炎和腦炎是病原體侵犯中樞神經系統而引發的疾病;這類病原體包括細菌(肺炎雙球菌、腦膜炎雙球菌、金黃色葡萄球菌等)、病毒(克沙奇病毒、腸病毒、皰疹病毒及日本腦炎病毒等)、以及其他種類微生物。臨床上可以診斷腦炎或腦膜炎的唯一檢查方法是腰椎穿刺,其作法是將穿刺針戳入脊椎管採集腦脊髓液(CSF)檢體,再送往實驗室檢查是否有發炎現象,然後再由醫師根據患者的病史、臨床表現和影像學檢查結果建議治療方式。由於檢查涉及侵入性過程,所以取自中樞神經系統(CNS)的樣品,其數量和可用性都受到侷限,因此大約有半數的急性腦膜炎及腦炎患者無法確認引發疾病的病原。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:張益祥/有勁基因
總體基因體學(Metagenomics)的概念是由Jo Handelsman等人於1998年所提出,意指特定環境(如:人類腸道、大自然環境)中所有微生物遺傳物質的總和。次世代定序(Next Generation Sequencing; NGS) 是總體基因體學的工具,透過次世代定序可以研究特定環境下微生物的組成與相對數量的多寡。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:洪郁豪/有勁生物科技
NGS次世代定序技術近年以其高正確率、高輸出量的優勢,刺激了總體基因體定序(Metagenomics Sequencing)技術以微生物相為對象的研究發展。國外的人體微生物相研究大型計畫─Human Microbiome Project,便是利用次世代定序技術,挑選16S rRNA中具鑑別度的部分區域進行定序,然後將大量的數據分析結果,與多種人類疾病做關聯,是為這類研究計畫的標竿之一。其他諸如糖尿病、炎症性腸病、自閉症等疾病研究,也都被陸續報導指出與人體微生物相息息相關。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:徐銘鴻/有勁生物科技
在科技越來越發達的現今,資訊業和金融業都在強調大數據分析;生物技術產業當然也不會放過這個機會,力圖將大數據分析結合醫療行為,開創出「個人化醫療」的未來新方向。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:張美虹 /有勁生物科技
對微生物群落的觀察研究來說,群落物種豐富度 (Species richness) 的測量可說是最簡單直觀的方式。此處要介紹如何進行 16S總基因體的物種豐富度分析。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:洪郁豪/有勁生物科技
精準總體基因體學 (Precision Metagenomics) ─利用總體基因學分析,快速診斷傳染性疾病並監控公共衛生
傳染病威脅著全球人口的健康,尤其會對抵抗力低下的醫院病患造成危害,因此,迅速確診病原是相當重要的工作。目前作為病原診斷的常用手段包括分離培養、目標基因片段增幅(targeted PCR)、微矩陣(microarray)鑑定及血清學分析等技術,花費的時間頗長,常需要數天至數週。此外,這些方法很難判斷傳染病為單一病原感染或是多病原共同感染所引起;在面對尚無法培養或完全寄生型病原微生物時更是棘手。不僅如此,選擇治療方法時,若無法確知病原的致病力,還容易造成抗生素的誤用或浪費,甚至產生抗藥性病菌。因此,利用最新生物技術改良過去傳染病病原的診斷方法,提高精確性的同時也縮短診斷的流程及時間,便是診斷技術很重要的改進方向。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:鍾婉嘉/有勁生物科技
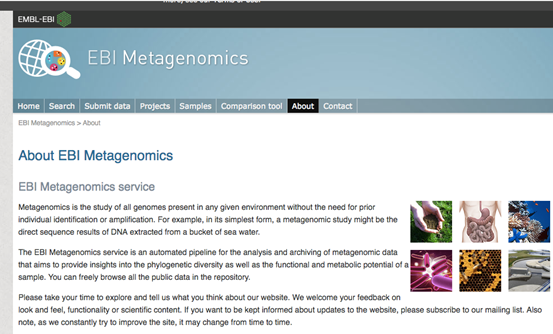
在做Metagenomics 分析時,大家很容易遇到的問題,便是專門資料庫的不足以及想要跟過去的研究比較時的困難性。在這裡我們介紹給大家一個Metagenomics 資料庫 – EBI Metagenomics (EMG) (Figure 1) 。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:紀雅齡/有勁生物科技
已知哺乳動物腸內道微生物族群的穩定性基於飲食習慣會有所變化,而在過去,大部分的實驗聚焦在細菌族群的改變上,在病毒上的所知並不算多。目前研究指出腸內道病毒群在克隆氏症及潰瘍性大腸炎的患者糞便中具有其獨特性,也有研究顯示飲食的改變會影響病毒群的分布,但詳細的原因還不清楚。
本實驗研究精緻醣類+ 高脂飲食,及高纖+ 低脂飲食狀態下的小鼠在改變飲食習慣、恢復原先飲食習慣後腸胃道微生物族群的改變,並對細菌與病毒的族群變動加以觀察比較。小鼠分為兩群,給予高脂或低脂飲食四周後,改成相反的飲食三周,再進入恢復原先飲食習慣的緩衝期三周,蒐集飲食改變及緩衝期期間糞便中微生物DNA 以檢測其微生物族群的改變。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:劉祥欽/有勁生物科技
對微生物而言,人體表面的皮膚就是一個擁有多樣棲地的完整生態系統。這些微生物像是細菌、真菌及病毒等,大多對人體無害或是有益,但有少部分微生物會造成粉刺、乾癬或是溼疹等常間的皮膚病。現在我們已經知道有些皮膚病好發在特定位置是因為致病病菌對生存環境的偏好所導致,例如導致濕疹的病菌偏愛潮濕的環境,而導致乾癬的病菌喜愛乾燥,所以濕疹好發在手臂或大腿的彎折處,而乾癬常在手肘和膝蓋上被發現1 , 2
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:陳崇斌/有勁生物科技
70年代的研究指出細菌細胞的數量是人類細胞數量的10倍,也就是說細菌的細胞數比上人類的細胞數是10:1,也有科學家推測是100:1,40年來我們都不曾去懷疑過人體身上的細菌數量比人體細胞多,直到2016年初的研究,重新估算了這個比值,認為是1:1 (Fig. 1),一舉推翻了過去幾10年來的估算結果,然而細菌的數量高估,不代表著他的重要性降低,相反的,細菌在人體身上扮演的角色一直被低估的;過去,總是認為這些細菌大多數都是對人體無益的,甚至是有害,受限於培養的研究方式,一直無法全面性的去了解人類身體上的菌群完整圖像,因為絕大部分的細菌是無法被培養的,這種以管窺天的研究方式,直到metagenomics與NGS技術發展,才得以有所突破。
Figure 1 比較1972年的文獻與2016年估算細胞量的方式的差異。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
作者:張美虹/有勁生物科技
在 16S metagenomics 中,操作分類單元 Operational taxonomic unit (OTU) 是根據序列的相似性做分類。其方法為叢集相似的 16S rDNA 基因序列的定序的片段。在每一個叢集中根據設定的序列相似性程度呈現一個 OTU ,形成的 OTU 可能為細菌的屬或種層級。一般而言,在 16S metagenomics 分析中 97% 或 99% 的序列相似性為典型的 OTU 叢集分析的門檻。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
隨著定序價格的降低,以及Illumina定序長度的增加,越來越多人改用Illumina HiSeq或MiSeq平台進行16S metagenomics sequencing 。定序所需之library製備方式,也不斷地在改進。以下列出幾種常見的幾種16S metagenomics sequencing之library製備方式,以及各自的優點與缺點。
採用 Barcoded 16S rRNA primer & Illumina TruSeq DNA Library Preparation
首先我們須先根據待定序的樣品數目, 設計不同的 16S-barcoded-primer。以16S的V1-V2 region為例,在27F以及338R primer 的5’端加上6-mer的barcod序列 (如下表,粗體底線的部分是barcode序列,其餘則是原本的16S primer序列)。
Yourgene Health 發表在 痞客邦 留言 (2) 人氣(
16S metagenomic sequencing 測不準的微生物community
目前能見度愈見增加的Single-cell sequencing是目前被看好的方法之一。簡單而言,藉由fluorescence-activated cell sorting (FACS)將微生物分出,再利用multiple displacement amplification (MDA)對單一細胞進行序列分析,可以僅針對有興趣的微生物族群做進一步的了解。
其序列可對應到已知基因及新陳代謝路徑,並提供對於菌系 (strain)變異性的評估證據,準確地完善原先無法被定義的演化樹分支 (Candidate division),賦予鄰近微生物物種原先16S metagenomics所欠缺的生物學及演化學定義。其提供的完整序列所帶來的意義為單單分析16S rRNA所無法提供的。
Single-cell sequencing所獲得的序列資訊能與其他metagenomic資料及metatrascriptomic資料相搭配,如同同時建構骨幹及血肉,將總體基因分析結果及深度定序資料彼此驗證;另外,由single-cell發展而來的mini-metagenomes亦為目前對於single-cell技術應用的熱門領域,藉由蒐集環境微生物取樣分析,為大環境生物演化的觀察提供良好的視野。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
VIDEO
傳統的微生物學,源自十七世紀中葉,荷蘭貿易商與科學家〜李文虎克( Antonie Philips van Leeuwenhoek )利用顯微鏡觀察自己口腔的微生物,開啟了微生物科學研究之基礎,後來陸續有科學家建立各式各樣的研究方法,通常都聚焦於少數種類的研究、分離與觀察鑑定等,但地球生物圈中有太多微生物是無法被分離培養研究的,迄今,微生物的研究手段更創新,巧妙的以核酸( DNA/RNA )角度進行微生物的分類。有鑑於此, Handelsman 等學者於 1998 年首先提出『總體基因體學( Metagenomics )』的概念,泛指研究環境某區域的所有微生物,利用特別的標誌基因【如:卡爾•烏斯( Carl Woese )提出的 16S rRNA 等】進行微生物的種類分析或功能性解讀。歷經傳統 Sanger 定序,到現在的次世代定序( Next Generation Sequencing , NGS ),總體基因體學的研究效能將更趨極致, NGS 定序科技的角色扮演更為舉足輕重。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
什麼是多樣性? 就從微生物當作例子說起吧!
人體的微生物對身體很重要,它們能保護人體健康,調節免疫系統,維護消化系統之運作。2013年興起了腸道環境與疾病相關議題,近期許多期刊上也相繼發表腸道環境(菌相)多樣性與疾病之相關性文獻。2013年6月份《自然Nature》期刊發表一篇文章,提及利用次世代定序儀器分別檢測代謝正常、不正常(血糖控制機能受損)與糖尿病之歐洲女性(平均年齡為70歲)之腸道環境(Gut metagenome)。結果發現,代謝不正常、糖尿病患者之腸道環境與代謝正常之腸道環境非常不同。那些代謝疾病之患者腸道環境改變,雖然腸道內之細菌數量一樣多但多樣性明顯較少。藉此推測,肥胖症、糖尿病與心血管疾病等相關代謝疾病與腸道環境之改變有關連。[1]
同樣地,2013年11月份,《科學Science》期刊發表兩篇[2、3],關於癌症治療效果與腸道環境相關之文章。通常,罹患癌症之患者體力不佳且免疫系統較弱,因此容易受到外環境影響而感染,因此需要藉由抗生素來幫助癌症患者抵抗外環境之感染。但抗生素之使用會影響腸道內菌群發展,而菌群多樣性卻被證實影響著癌症患者接受化療的效果程度。《科學Science》期刊發表兩篇文獻內容皆以動物實驗為模組,結合次世代定序技術檢測腸道環境與癌症之腫瘤微環境的關係,並且指出腸道微生物能夠幫助癌症治療效果。不過,文獻中有提及,這些模組皆作用於動物體上,同時也期望未來在人體試驗上能夠看見署光。
不只腸道環境需要多樣性能夠維持人體健康,人體的免疫系統,同樣也需要多樣性,來維持與調節免疫系統。免疫系統是最了解自體的醫生,當免疫系統發生問題,那麼與免疫相關之疾病當然紛紛出現,因此,若能了解免疫醫生如何診斷與治療人體,那麼疾病也就更容易對付了。早在2009年PNAS[4]文獻發表,利用次世代定序儀器對免疫T細胞接受器( T Cell Receptor,TCR)的特地區域做定序,發現腸癌患者之免疫細胞多樣性比正常人少,免疫細胞的多樣性低及表示功能性較少,即便是免疫細胞總數不變,那麼面對疾病就相對變得難解了。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
et al. , 1995),因此,80年代發展出非培養的研究方式(cultured independent method),包含T-RFLP、DGGE、SSCP、以及cloning and sequencing的方式來研究環境微生物的族群 (Nocker et al. , 2007),以上方式,皆是針對族群共有的目標基因的amplicons來分析,目標基因是依據不同的觀察目標而有所差異,常用的基因有18SrRNA (Eukaryotic microbes)、ITS (Eukaryotic microbes)、Bacterial 16S rRNA、Archaea 16S rRNA、與一些功能性的基因 (如 psbA、psaB、amoA與amoB)。T-RFLP、DGGE、SSCP、以及cloning and sequencing四種方式中,以cloning and sequencing的方式能夠提供最精確的資訊 (表一),然而,在面對高度複雜的環境生態時,必須挑選許多clone去進行定序,才能足以呈現真實的物種組成,例如,至少需要定序1000個clone才能夠呈現沿岸海水的細菌族群圖譜 (Acinas et al ., 2004)。
從2006年開始有研究利用目標基因amplicons (如 bacterial V6),直接進行次代定序,即所謂的Amplicons high throughput sequencing,不但可以免除cloning繁複的流程,而且可以獲得大量的序列資訊 (Sogin et al., 2006),以Illumia定序技術定序平台為例,一次可以得到超過100,000,000條序列,這種方式同時擁有高輸出量以及高精確度的特性,因此能夠精確地呈現高度複雜的微生物族群圖譜 (表一)。這種amplicons的定序還能夠配合multiplexing(註一)的方式,讓兩種以上來源的樣品同時進行定序,使的定序更加有效率 (Binladen et al ., 2007)。這樣的實驗方式已經被廣泛利用,包含人類共生菌的研究 (Huse et al ., 2008 and Hummelen et al., 2010)、海水菌相研究 (Anderssonet al., 2010)以及土壤環境研究 (Chu et al., 2010)。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
想知道某些環境因子的改變(如:生病的腸子或加了料的海水)會使環境中的某群生物(如:細菌或浮游生物)在群聚結構或基因表現有何反應嗎?2012 年2 月的PNAS 剛好就有篇paper 利用metatranscriptome 分析Fe2+ 離子缺乏的海水加料( 阿就是Fe2+ 離子) 後,其藻相與基因表現是如何反應的[1] 。
圖1. 紅色與綠色區域為HNLC ,位置分別在南大洋、太平洋赤道區域、北太平洋副極區 (http://www.geos.ed.ac.uk/homes/s0675905/MScBSc.html
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(
現代人長時間生活在辦公室的空間,工作空間裡潛藏了許多的細菌,與我們朝夕相處的細菌到底有多少?有哪些種類的細菌?這些細菌會致病嗎?辦公室的哪些地方有特別多細菌?男生所處的環境真的比女生擁有更多的細菌嗎? Hewitt 的研究團隊1 在美國的三個不同城市,隨機挑選九十個辦公室,針對每個辦公室裡的椅子、電話、電腦、滑鼠、鍵盤及桌面約13平方公分面積的區域做細菌採樣,而這些辦公室的使用者分別為男女生各半。首先,作者將樣品稀釋後塗在 R2A media 的培養基上,經過五天的培養,統計樣品內的菌量,結果如下圖所示,橫軸及縱軸代表的意義分別為樣品的來源及細菌的數量,結果顯示椅子及電話上的菌量高於桌面、鍵盤及滑鼠,另外,男性使用的辦公用品得到的菌量比女性的多,而在不同城市的來源上,舊金山的辦公室菌量是三個城市中最低的,上述的菌量的差異作者使用ANOVA分析的確是有意義的差異性。
在菌種分析上,由於環境中的細菌組成複雜,無法以培養方式辨別樣品裡面所有的細菌種類,所以作者先將樣品中的DNA萃取出來,以PCR的方式將16S rRNA基因的高度變異區放大,並且將此產物以NGS技術定序,並且分析這些序列以得到細菌的種類。結果顯示這些辦公室用品附有二十種門中超過五百屬的細菌,其中含量最多的為變形菌門(Proteobacteria),其他比例由高至低依序是 厚壁菌門(Firmicutes)、放線菌門( Actinobacteria) 及 擬桿菌門 Bacteroidetes ,不同樣品細菌種類的相對比例圖如下。
與之前做人體各部位菌相的研究相比較 2.3.4 ,辦公室環境中的細菌種類大多也出現在皮膚及口腔,另外特別的是,部分的種類與在人體的消化道內的菌種相同,辦公室細菌種類中,也有些會出現在土壤裡面的細菌,這些結果可以協助推測可能的細菌來源。
Yourgene Health 發表在 痞客邦 留言 (1) 人氣(
你知道嗎? 細菌族群就棲身在你的身體裡,有些住在皮膚表面,有些居住在腸內道,而不同部位的細菌族群種類也不盡相同,甚至,每個人身體上的菌相也會有所差異;2009年,美國科羅拉多大學團隊,利用NGS系統進行16S rRNA序列分析,進而描繪出全世界第一張人體菌相圖(上圖),讓我們清楚得觀察到,不同部位皆有其獨特的細菌族群,而口腔與腸道是人體菌相最複雜的地方,相較而言,皮膚表面的菌相就顯得單純;有越來越多證據顯示,人類身體的細菌族群與人體健康有關,然而,人體共生菌方面的研究仍在剛起步的階段,這群細菌的所扮演的角色還待更進一步的研究。
Yourgene Health 發表在 痞客邦 留言 (1) 人氣(
Metagenomics 這十年來才發展出來的新學門,主要是透過研究分析環境基因體,進而來描繪環境的代謝特性。
一個完整的環境系統,是由許多種生物組成,這些生物種類包羅萬象,除了肉眼可見的動植物外,還有肉眼看不見的微生物族群,這個族群數量遠比動植物多,包含真核微生物(Eukaryotic microbes)、細菌(Bacteria)、古生菌(Archaea)以及病毒(Virus),然而,百分之99以上的微生物是無法培養的,欲描繪一個真實環境的生化代謝圖譜,最有效的方式就是直接萃取環境中的DNA或RNA加以分析,藉由這些基因體資訊,來對環境有一個全盤性的了解。環境基因體具有高多樣性以及高複雜度,最有名的例子是,Craig Venter從一桶海水中萃取細菌DNA,經過基因體分析後,發現含有150,000,000bp非重複性的鹼基對、1,800個genotype以及1,200,000個過去沒有被記錄過的基因,因此,要描繪出真實的完整的環境基因體特性,需要大量的資料量 (Venter et al. , 2004)。為了研究高度複雜的環境基因體,近期發展出兩個學門Metagenomics與Metatranscriptomics;Metagenomics是在DNA的層級,來分析環境基因體;而Metatranscriptomics是以RNA的層級來分析,可以補強Metagenomics不足的部分,除了可以分析各種基因的表現量,還能夠偵測環境中的RNA病毒族群。
早期Metagenomics與Metatranscriptomics實驗流程中,必須將環境的基因體DNA或cDNA轉植到E. coli體內,再進行定序分析,其過程繁瑣而冗長,而且得到的資訊量相對有限 (Trings et al. , 2005);現在metagenomics研究,可以跳過繁瑣的分子生物學實驗技術,只需要將環境中的DNA或cDNA,直接進行次代定序(next generation sequencing)。 隨著定序技術的發展,定序資料的輸出量也越來越高,也就能夠呈現基因體真實的樣貌,至2010年,一次NGS定序所能夠得到的資料量已經達到100Gb的等級,因此,面對高度複雜的環境基因體的研究,NGS是最有效率的工具。
Yourgene Health 發表在 痞客邦 留言 (0) 人氣(








 {{ article.title }}
{{ article.title }}
