作者:李覺白/有勁生物科技
RNA-Seq可幫助科學家偵測所有表現的基因,即使是尚未發現的基因也可被偵測,因此能應用於找尋新的基因;延伸的應用包含找尋一些和基因的結構相似但不會轉譯成蛋白的non-coding RNA及基因表現時因同一個基因下選擇性剪接產生(Alternative splicing)的isoform。
在RNA-Seq的實驗設計中,定序深度是很重要的因子,定序深度會與transcriptome size有相關,一般而言genome size越大的物種,其transcriptome size就越大,定序的深度也需要更高。下表初略將不同物種的transcriptome size分類
|
Organism |
Transcriptome Size (Estimate) |
|
Unicellular (Bacteria, Yeast) |
0.8 – 3.0 Mb |
|
Multicellular Invertebrate (Worms, Flies) |
10 – 50 Mb |
|
Complex Multicellular (Plants, Vertebrates, mammals, humans) |
30 – 200 Mb |
假如一次實驗的定序深度不夠,會影響到基因定量的準確度。因為不同基因的表現量的大小差距是非常大,在定序量不足的情況下,低表現量的基因(low-abundance genes)就有可能會因此沒被定量到。
估計RNA-Seq定序深度對於實驗是非常重要,在此印度的Ganit Labs發展了一個幫助科學家方便估計RNA-Seq定序量的App,RNAtor,方便科學家在定序前估計所需要的定序量,目前提供Android的版本。
RNAtor的初始介面如下

1)輸入物種名稱或直接給予transcriptome size

2)預期的fold change (於實驗組及對照組下相同的基因表現倍數變化)
3)實驗設計上要有幾次的技術性重複(technical replicates)。

使用物種為人類,fold change為3倍,要有3次technical replicates的估計定序量為452.56 million reads。
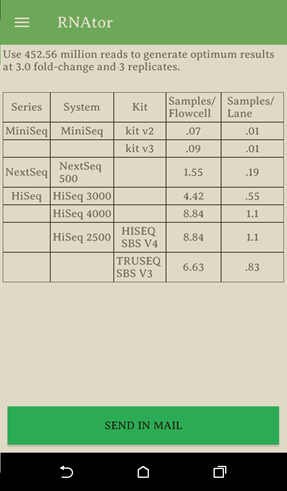
由於transcriptome size是必須要有的值,假如使用者真的不知道自己研究物種的transcriptome size, RNAtor建議可用genome size的10%來估計。
參考資料:




 留言列表
留言列表 {{ article.title }}
{{ article.title }}
